Determinación de la curva de crecimiento microbiano
Saccharomyces Boulardii en tunta variedades chaska y negra
Determination of the microbial growth curve of Saccharomyces
Boulardii in tunta chaska
Martha Rodriguez Molina1 Alex Danny Chambi Rodriguez2 ]]>
1Centro de Investigacion de Tecnologia de alimentos, Escuela Profesional de Ingeniería de industrias alimentarias, Universidad Peruana Unión, Lima-Perú
elenicemartha2013@gmail.com
2Centro de Investigacion de Tecnologia de alimentos, Escuela Profesional de Ingeniería de industrias alimentarias, Universidad Peruana Unión, Lima-Perú.
adanny@upeu.edu.pe
Artículo recibido: 29-01-2019 Artículo Aceptado: 25-04-2019
Resumen
La finalidad de la presente investigación fue determinar la curva de crecimiento microbiano Saccharomyces Boulardii (SB) en tunta variedades Chaska y Negra mediante modelamiento matemático, aplicando las ecuaciones de Gompertz y Logistico en la cual se realizó cuatro tratamientos que constaron de mezclas en matraces de 250 ml entre agua destilada Chaska (T1); agua destilada Negra (T2); Solución Salina Peptonada Chaska (T3); Solución Salina Peptonada Negra (T4); para posteriormente ser esterilizadas a 121 °C por 15 min, luego se paso a inocular SB a 37 °C con agitación constante de 20 RPM por un lapso de 7 horas; donde en intervalos de una hora se realizó las lecturas del incremento de biomasa con un microcospio y cámara neubauer expresado en unidades formadora de colonias por mililitro (ufc/ml); asimismo se realizó una comparación del pH, °Brix y acidez entre las variedades de tunta en tiempos de fermentación de 24 y 48 horas; los resultados del modelamiento matemático nos dio que gráficamente los tratamientos T1 y T4 presentan similitud; asimismo este fenómeno se repite en los tratamientos T2 y T3; por otro lado en la bondad de ajuste de los parámetros de cada uno de los modelos mostro una variedad de datos donde se le puede otrogar varias aplicaciones; finalmente con respecto al pH y la acidez ambos incrementaron siendo más notoria en 48 horas.
Palabras Clave. Saccharomyces Boulardii, Tunta, Gompertz, Logistico.
The purpose of this investigation was to determine the curve of microbial growth of Saccharomyces Boulardii (SB) in tunta Chaska and Negra through mathematical modeling. The Gompertz and Logistico equations were applied in four treatments. The first was a mixture in 250 ml flasks between distilled water - Chaska (T1); the second distilled water - Black (T2); the third Salina Peptonada Solution - Chaska (T3); and the last Peptonada Saline Solution - Black (T4). These treatments were sterilized at 121 ° C for 15 min, then SB was inoculated at 37° C with constant agitation of 20 RPM for a lapse of 7 hours; where, at intervals of one hour, the readings of the biomass increase were made with a microcosp and a neubauer chamber expressed in colony forming units per milliliter (cfu / ml); Likewise, a comparison of the pH, °Brix and acidity between the tunta varieties was made in fermentation times of 24 and 48 hours. The results of the mathematical modeling showed that graphically the T1 andT4 treatments are similar; also, this phenomenon is repeated in treatments T2 andT3. On the other hand, in the goodness of fit of the parameters of each model showed a variety of data that can give several applications. Finally, with respect to pH and acidity both increased being more noticeable in 48 hours.
Key words. Saccharomyces Boulardii, Tunta, mathematical modeling.
Introducción
En actualidad el desarrollo de alimentos funcionales esta adquiriendo mucha fuerza, ya que surge la necesidad de que los alimentos no solo cumplan la función nutricional sino también medicinal; dando asi como resultado la denominación de "alimentos funcionales"; puesto que estos cumplen el rol de un medicamento, tal es el caso de los microorganismos liofilizados utilizados para el tratamiento de enfermedades gastrointestinales como es el caso de Saccharomyces boulardii, que es considerado un probiótico debido a la acción bioquímica que produce en su recorrido por el tracto gastrointestinal, generando efectos fármaco dinámicos semejantes a los efectos fisiológicos de la flora intestinal normal; es por eso que esta levadura es una opción para el desarrollo de nuevos alimentos con características probióticas haciendo simbiosis entre el alimento y el microorganismo mencionado (Peña, 2007).
Existen estudios de entre los cuales destacan la viabilidad de la adición de SB en quesos demostrándose que este microorganismo puede mantenerse viable y activo de modo que esta al ser ingerida pueda dar los beneficios antes mencionados (Vega, Martinez, Montañez, & Rodiles, 2016); asimismo; Swieca et al., (2019) demostró que, el uso de SB en brotes de frijol adzuki, mejora las propiedades nutricionales que son favorables para la salud . Por otro lado Trigueros et al., (2016) destaca el uso del suero de leche como un buen medio de cultivo para este microorganismo, ya que genera como resultado de sus reacciones bioquimicas metabolitos como síntesis de la glucosa.
Por otro lado, la tunta es un alimento ancestral del altiplano peruano, elaborado mediante un proceso de deshidratación de tuberculos a través de sucesivos congelamientos (con protección solar), sumergido en agua corriente (río) y secado al sol. (Guidi et al., 2002) debido a este proceso el tubérculo presenta características parecidas a la papa liofilizada, con bajo contenido de agua, siendo necesario hidratar la tunta para luego ser preparada en las comidas, es debido a esta característica que el agua puede ser útil para el transporte de compuesto químicos y biológicos como sales y microorganismos.
Por tal motivo el objetivo de esta investigación es determinar la curva de crecimiento microbiano de Saccharomyces Boulardii en Tunta provenientes de las variedades de papa Chaska y Negra.
]]>Metodología
Cepas de levadura y condiciones de crecimiento
Todos los experimentos se realizaron con cepas liofilizadas de saccharomyes Bouardii (Floratil 200 mg.) en medios líquidos (agua destilada y Solución salina peptonada) enriquecidos con tunta provenientes de las variedades de papa Chaska y Negra; de las cuales se procedió a esterilizar en matraces de 250 ml, en autoclave marca STURDY a 121 °C por 15 min, parámetros bajo los cuales se evita la interferencia de otros microorganismos asegurando la esterilidad de los medios.
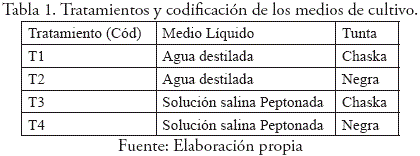
A partir de estos se preparó una batería de 4 matraces, conteniendo 200 ml aproximados entre tunta y medio líquido, de esta manera se obtuvo 4 tratamientos codificados según se muestra en la Tabla 1, para así luego inocular las cepas de SB a temperatura de 37 ± 1 °C, asimismo se incubo a la misma temperatura con una agitación constante de 20 RPM regulado por un baño maria BS - 11 y cada una hora (0-7 horas de incubación) se retiraba cada matraz para el conteo correspondiente.
Crecimiento microbiano y modelamiento matemático.
Para las lecturas del incremento de biomasa se utilizó un microcospio monocular LW SCIENTIFIC y una cámara neubauer de 0,100 a 0,00025 mm2 expresando los resultados en unidades formadora de colonias por mililitro (ufc/ml) convertidos a logaritmos de base 10 y modelados en ecuaciones presentados en la Tabla 2; aplicando un análisis de regresión no lineal en el paquete estadístico Statsoft Statistica v. 13.0.
La comparación de los diferentes modelos ajustados, se realizó tomando la factibilidad de los mismos para alcanzar el ajuste, determinando los parámetros de crecimiento correspondientes a cada modelo matemático (Castro et al., 2008).
]]> Donde N es el número de microorganismos a un tiempo t, N0 > 0 es el número de microorganismos en momento inicial, el parámetro C > 0 es tasa especifica de crecimiento, el parámetro B es velocidad máxima específica y M es el tiempo requerido para hallar B (Coll, Giannuzzi, Noia, & Zaritzky, 2001).Modelos de bondad de ajuste.
Para realizar el ajuste de los modelos para cada tratamiento se aplicó los análisis estadisticos sugeridos por Torres, Barbosa, Meyer, Noda, & Sarduy (2012) de: coeficiente de determinación R2 y cuadrado medio del error.
Análisis de pH, °Brix y Acidez
Asimismo, se realizó un análisis de los grados brix (°B), pH y acidez, a las 24 y 48 horas. El análisis de °B fue realizado según el procedimiento de la (AOAC -Official Method 932.12, 1990) con un refractómetro 0 -32. El pH se hizo empleando un potenciómetro marca HANNA (AOAC 32.018, 1984) y finalmente para la determinación de acidez se aplicó el procedimiento de la AOAC 947.05, (1990) que consiste en titulación acido base con hidróxido de sodio (NaOH) a una concentración de 0,1 N con indicador fenolftaleína al 1%, expresados en porcentaje de acidez láctica ya que SB es una bacteria láctica (Sánchez, Ruiz, & Morales, 2015).
Resultados y discusiones
Crecimiento microbiano
La tabla 3 muestra las lecturas del crecimiento microbiano de cada uno de los tratamientos, en ella se aprecia que al tiempo siete, T4 presenta una mayor cantidad de ufc (6,43) que corresponde a la composición solución salina peptonada - Negra, seguido de T3 (6,42) constituida por agua destilada Negra, sin embargo la DE de T4 es mayor que la T3; asimismo T1 y T2 presentan valores de 6,38 y 6,25 de ufc respectivamente también se observa que la DE deT2 es mayor a la de T1.
]]> Según Mantilla, Mendoza, & Oviedo, (2010) en su investigación de selectividad de medios de cultivos para levaduras del género Candida sp describe que las levaduras pueden crecer en medios complejos naturales como es el caso de la guayaba agria demostrando que incluso esta puede ser mejor que medios comerciales; es así que debido a la diferentes composiciones de los tratamientos se pudo observar que las enriquecidas con la tunta de la variedad de la papa Negra (T3 y T4) proporciona mejor medio de crecimiento frente a los tratamientos con la tunta proveniente de la variedad Chaska.
Modelamiento Matemático.
En la figura 1 se puede apreciar las curvas sigmoideas del modelo de Gompertz correspondientes a cada uno de los tratamientos, en ella se aprecia que T2 y T3 presentan similitud, así como las de T1 y T4.
Por otro lado, tenemos los parámetros del modelo matemático en la Tabla 4 donde se tiene que T4 presenta la mayor tasa específica (C)con respecto a los demás tratamientos, seguido por T3; con respecto a la velocidad máxima específica (B) se muestra con mayor velocidad en T1 y T4 siendo el primero mas veloz, y T2 y T3 con las más bajas velocidades; con respecto al tiempo requerido para hallar B (M) se muestra que T2 se presenta en menos tiempo seguido de T3 y finalmente por T1 y T4; y finalmente el nivel de correlación de cada uno de los tratamientos es superior a 0,8 dándonos un buen ajuste en cada uno de ellos.
En la figura 2 se puede apreciar las curvas sigmoideas del modelo Logístico correspondientes a cada uno de los tratamientos, en ella se aprecia el mismo fenómeno de la figura 1.
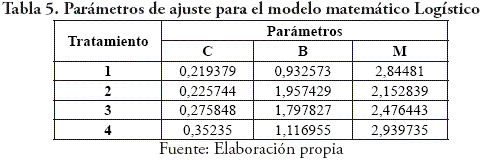
Por otro lado, tenemos los parámetros de ajuste para este modelo en la Tabla 5 donde se tiene que T4 presenta la mayor tasa especifica (C) con respecto a los demás tratamientos, seguido por T3; con respecto a la velocidad máxima especifica (B) se muestra con mayor velocidad en T1 a diferencia de los otros tratamientos; con respecto al tiempo requerido para hallar B (M) se muestra que T2 se presenta en menos tiempo seguido de T3 y finalmente por T1 y T4.
]]>
Tanto en la figuras 1 y 2 se muestra las curvas de crecimiento de SB que según (Castro et al., 2008), en la investigación de modelos cinéticos aplicados al crecimiento de lactococcus lactis subsp. lactis en leche, demuestra que, a diferencia de los modelos de regresión lineal simples, los modelos de regresión no lineal son mejores ya que estos pueden presentar gráficos como los obtenidos en los cuales se pueden determinar las fases de crecimiento de los microorganismos, siendo que para T2 y T3 gráficamente se podría realizar esta operación en ambos modelos aplicados, a diferencia de T1 y T4.
Vanegas & Ramírez, (2016) en su estudio del crecimiento de Pseudomonas aplicando el modelo de Gompertz, Logistico y Baranyi, describe que el modelo de Gompertz es óptima en la contrucción de las curvas de crecimiento microbiano de modo que los resultados obtenidos corroboran lo desmostrado en el presente trabajo.
Modelos de bondad de ajuste.
La tabla 6 muestra los criterios estadisticos para los modelos y tratamientos se puede apreciar que la bondad de ajuste en cada uno de los criterios de ajustan al modelo Logistico.
Los valores de los criterios estadisticos analizados son corroborados por Torres et al., (2012); puesto que en su estudio demostroque la el modeloLogistico presenta un mejor ajuste.
pH, °Brix y Acidez
La tabla 6 muestra que SB puede reducir la concentración de pH en ambas variedades con respecto al tiempo, lo mismo que con la acidez, sin embargo, en la variedad chaska no se vio esta diferencia, por otro lado, con respecto a los °Brix se puede apreciar un incremento en ambas variedades con respecto al tiempo.
]]> El incremento de los grados °Brix según Rodríguez et al., (2006) se debe a que las levaduras en medio de sustratos ricos para su crecimiento pueden generar enzimas que degradan los almidones es asi que por esta razón los carbohidratos son degrados en azucares simples como glucosa, asimismo; Ortiz et al.,(2008) menciona que, las levaduras del genero Saccharomyces tienen la capacidad de degradar muchos sustratos; León et al., (2006) en su estudio de fementacion de masas agrias demostró que el fenómeno de variación de pH y acidez se debe al metabolismo de las levaduras sobre los sustratos en donde se encuentran. Por otro lado, Swieca et al., (2019) muestra que el microorganismo aporta al alimento propiedades nutricionales por efecto del metabolismo de este, haciendo del alimento más nutritivo para quien lo consume. Finalmente Vega et al., (2016) mediante la aplicación de SB demostró que es posible el desarrollo de este tipo alimentos, ya que estos pueden mantenerse viables y activos.
Conclusiones
Mediante el modelado matemático se logro obtener las curvas de crecimiento microbiano, estas fueron muy precisos para describr los comportamientos de saccharomyces boulardii en medios enriquecidos con tunta; ya que en las gráficas en algunas se puede identificar claramente las fases de crecimiento microbiano en especial para los tratamientos 2 y 3.
Asimismo se obtuvo los parámetros microbiológicos que permiten decribir el comportamiento adecuado de la curva de crecimiento que permiten predecir, determinar condiciones optimas para el crecimiento microbiano y asi aprovechar cada una ellas a diferentes aplicaciones.
Finalmente, resulta importante seguir con estudios que permitan la utilización de sustratos como la tunta y modelos matemáticos para el desarrollo de productos probióticos.
Notas
1 Ingeniero de Alimentos.
2 Ingeniero de Alimentos. Maestrante en Ciencia y Tecnología de Alimentos. Especialista en Microbiología de Alimentos
]]>Referencias Bibliográficas.
AOAC -Oficial Method 932.12. (1990). Fruits and fruit products. Solids (Soluble) in Fruits and Fruit Product: Refractometer . AOAC International. [ Links ]
Castro, G., Valbuena, E., Sánchez, E., Briñez, W., Vera, H., & Leal, M. (2008). Comparación de modelos sigmoidales aplicaddos al crecimiento de Lactococcus lactis subsp. lactis. Revista Científica FCV-LUZ, XVIII, 582-588. [ Links ]
Coll, F., Giannuzzi, L., Noia, M., & Zaritzky, N. (2001). El Modelado Matematico: Una Herramienta Util para la Industria Alimenticia. Ciencia Veterinaria., 22-28. [ Links ]
Guidi, A., Esprella, R., Aguilera, J., Devaux,A. (2002). Características de la Cadena Agroalimentaria de Chuño y Tunta para el Altiplano Central de Bolivia. Cochabamba. Bolivia. PROINPA. [ Links ]
León, P., Ángela, M., Montoya, C., Olga, I., Karina, E., Diana, M., & Juan, M. (2006). Bacterias ácido lácticas (BAL) silvestres colombianas presentan propiedades adecuadas para la fabricación de masa ácida. Vitae, 13(2), 26-35. [ Links ]
Mantilla, C., Mendoza, C., & Oviedo, L. (2010). Productividad y selectividad del medio de cultivo a partir de guayaba agria (Psidium araca) en el crecimiento de levaduras nativas del género Candida sp. Revista Colombiana de Biotecnología, 12(2), 116-123. [ Links ]
Ortiz, A., Reuto, J., Fajardo, E., Sarmiento, S., Aguirre, A., Arbeláez, G., Quevedo-Hidalgo, B. (2008). Evaluación de la capacidad probiótica "in vitro" de una cepa nativa de Saccharomyces cerevisiae. Redalyc, 13(2), 138-148. [ Links ]
Peña, A. S. (2007). Flora intestinal, probióticos, prebióticos, simbióticos y alimentos novedosos. Revista Espanola de Enfermedades Digestivas, 99(11), 653-658. [ Links ]
Rodríguez, Z., Boucourt, R., Rodríguez, J., Albelo, N., Nuñez, O., & Herrera, F. R. (2006). Aislamiento y selección de Microorganismos, con capacidad de degradar el almidón. Revista Cubana de Ciencia Agrícola, 4(3), 349-354. [ Links ]
Sánchez, M., Ruiz, M., & Morales, M. (2015). Microoganismos probióticos y salud. Ars Pharmaceutica, 56(1), 4559. [ Links ]
Swieca, M., Kordowska, M., Pytka, M., Gawlik, U., Seczyk, L., Zlotek, U., & Kapusta, I. (2019). Nutritional and pro-health quality of lentil and Swieca, M., Kordowska-Wiater, M., Pytka, M., Gawlik-Dziki, U., Seczyk, L., Zlotek, U., & Kapusta, I. (2019). Nutritional and pro-health quality of lentil and adzuki bean sprouts enriched with probiotic yeast. LWT - Food Science and Technology, 100(June 2018), 220-226. [ Links ]
Torres, V., Barbosa, I., Meyer, R., Noda, A., & Sarduy, L. (2012). Criterios de bondad de ajuste en la selección de modelos no lineales en la descripción de comportamientos biológicos. Revista Cubana de Ciencia Agrícola, 46(4), 345-350. [ Links ]
Trigueros, D., Fiorese, M., Kroumov, A., Hinterholz, C., Nadai, B., & Assunção, G. (2016). Medium optimization and kinetics modeling for the fermentation of hydrolyzed cheese whey permeate as a substrate for Saccharomyces cerevisiae var. boulardii. Biochemical Engineering Journal, 110, 7183. [ Links ]
Vanegas, D. M., & Ramírez, M. E. (2016). Correlación del crecimiento de Pseudomonas fluorescens en la producción de polihidroxialcanoatos de cadena media (PHAMCL) mediante modelos primarios de Gompertz, logístico y baranyi. Informacion Tecnologica, 27(2), 87 96. [ Links ]
Vega, R., Martinez, H., Montañez, J., & Rodiles, J. (2016). Viabilidad de Saccharomyces boullardii en queso fresco bajo condiciones de acidez "in vitro." Nova Scientia, 7(15), 68. [ Links ]
]]>