Alternativas de diagnóstico de laboratorio para la detección del virus de la Influenza
Laboratory diagnostic alternatives for the detection of Influenza virus
Cecilia Angulo Valdivia1, Nattaly Grecia Torrico Villarroel2
1Bióloga - M.Sc. en Biología, Laboratorio de Biología Molecular-Instituto de
Recibido el 26 de septiembre de 2019.
]]> Aceptado el 03 de diciembre de 2019
El virus de la Influenza (Flu) ha sido causante de diversas pandemias que han producido millones de muertes a nivel mundial, siendo necesario un diagnóstico diferencial al producir un cuadro clínico similar al de infecciones producidas por otros virus respiratorios. El diagnóstico oportuno y certero de infección por Influenza virus empleando pruebas de laboratorio, permite una mejor toma de decisiones en el ámbito médico, de tal manera que se pueda administrar un tratamiento adecuado, disminuir complicaciones y costos de hospitalización. A pesar de existir diferentes alternativas de métodos de diagnóstico, desde técnicas tradicionales como el cultivo viral o la inmunofluorescencia, hasta técnicas de detección de ácidos nucleicos, todas presentan ventajas y desventajas en cuanto al tiempo de procesamiento y entrega de resultados, sensibilidad, especificidad, experticia del personal, costos e infraestructura del laboratorio, siendo estos factores importantes a considerar para la implementación de nuevas técnicas en los laboratorios clínicos.
The Influenza virus (Flu) has been the cause of several pandemics that have produced millions of deaths worldwide, requiring a differential diagnosis to produce a clinical picture similar to infections caused by other respiratory viruses. The timely and accurate diagnosis of infection by influenza virus using laboratory tests, allows better decision making in the medical field, so that appropriate treatment can be administered, reduce complications and hospitalization costs. Despite the existence of different diagnostic methods alternatives, from traditional techniques such as viral culture or immunofluorescence, to nucleic acid detection techniques, all of them have advantages and disadvantages in terms of processing time and delivery of results, sensitivity, specificity, laboratory expertise, costs and infrastructure. These factors are important to consider for the implementation of new techniques in clinical laboratories.
Keywords: Influenza, diagnosis, laboratory.
La influenza, también conocida como “Flu” o gripe, es una infección viral aguda de las vías respiratorias con síntomas parecidos al resfrío común1,2. Las infecciones por influenza pueden generar neumonía e insuficiencia respiratoria aguda, complicándose por la coinfección bacteriana3.
La influenza puede tener un comportamiento endémico, epidémico o de pandemia2, especialmente en estaciones de invierno. Los tipos A y B causan epidemias estacionales de influenza4. Hasta la fecha se han reportado que las pandemias por influenza causaron la muerte de aproximadamente 60 millones de personas5. Las pandemias, están relacionadas con la aparición de una cepa recombinada que a menudo provoca un aumento de la morbilidad con un enorme impacto clínico y económico3. Por lo que el diagnóstico de la influenza es importante para la toma de decisiones en el manejo del paciente6.
Revisión bibliográfica
El diagnóstico oportuno de Influenza continúa siendo un desafío para la salud pública, ya que, según la Organización Mundial de la salud, las epidemias de Influenza causan de 3 a 5 millones de casos severos y de 300 000 a 500 000 muertes a nivel mundial cada año7. En el caso de Bolivia, para el 2019 el porcentaje de positividad para influenza aumentó con la circulación concurrente de los virus A(H3N2), A(H1N1) pdm09 y B8. En nuestro medio, a pesar de la incidencia de la Influenza, las alternativas de diagnóstico siguen siendo limitadas por los costos y accesibilidad a estos servicios.
A pesar de que nuevos medicamentos antivirales están disponibles para tratar las infecciones por influenza tipo A y B, en la práctica clínica estos son utilizados sin antecedentes de diagnóstico laboratorial o los síntomas son confundidos proporcionándose antibióticos innecesarios1,3, además de incrementar costos asociados a los cuidados de salud hospitalarios9. Por lo que la detección temprana y eficaz de estos agentes es importante para implementar una terapia antiviral oportuna y adecuada9.
Al ser la Influenza A el único género capaz de producir pandemias, la investigación para diagnosticar los subtipos frecuentes y nuevos, según su clasificación de naturaleza antigénica y genética de sus glicoproteínas de superficie6, constituye un objetivo significativo para toma de decisiones clínicas y epidemiológicas10, remarcando la importancia de establecer un diagnóstico de laboratorio definitivo6.
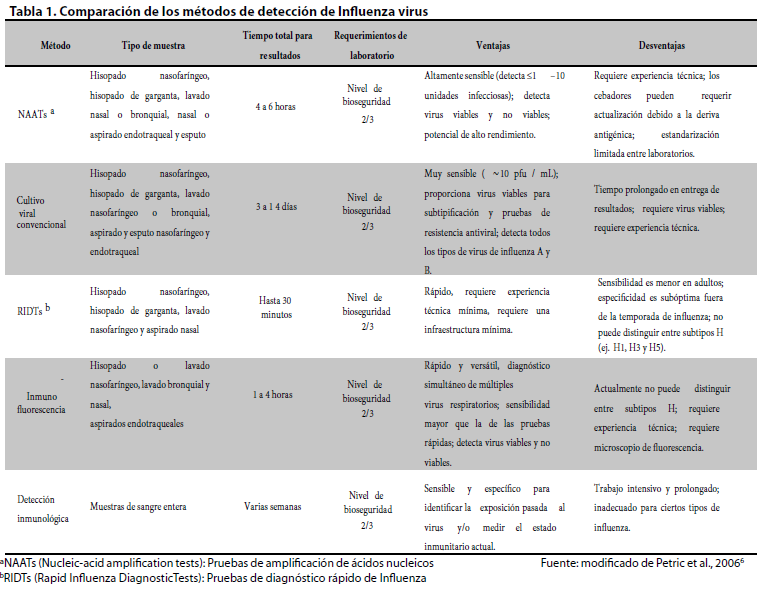
Todas las pruebas de laboratorio presentan limitantes, según la disponibilidad, el costo y el rendimiento de las técnicas de diagnóstico11 (Tabla 1). Actualmente existen 64 exámenes de diagnóstico para Influenza virus aprobados por la FDA (Food & Drug Administration, por sus siglas en inglés)12.

A continuación, se describen las diferentes pruebas de laboratorio disponibles para el diagnóstico de la Influenza, con sus correspondientes ventajas y desventajas. Es importante mencionar que, para obtener resultados fiables en el diagnóstico, las condiciones de la muestra son fundamentales.
Condiciones de la muestra biológica
El principal requisito a la hora de valorar las muestras obtenidas a partir del tracto respiratorio es que estas deben contener el mayor número posible de células epiteliales ciliadas, donde los virus respiratorios replican13. En este sentido, las muestras más apropiadas son las obtenidas del tracto respiratorio superior, siendo tomadas de las fosas nasales profundas (hisopado nasal), faringe (hisopado faríngeo) y nasofaringe (hisopado nasofaríngeo), aspirado nasofaríngeo y el aspirado bronquial14.
La excreción de partículas virales a partir de la aparición de los síntomas desciende progresivamente con el paso de los días en el paciente inmunocompetente. La toma de muestra debe ser realizada antes de las 48 a 72 horas del comienzo de los primeros síntomas13. El transporte de las muestras al laboratorio debe realizarse en un plazo de entre 24 y 48 horas, a una temperatura de entre 2 y 8 °C, con objeto de asegurar la viabilidad de las partículas virales o la integridad del material genético13.
Los métodos de laboratorio disponibles para el diagnóstico de Influenza que se describen a continuación corresponden a pruebas utilizadas tradicionales como a técnicas recientes.
Detección molecular: pruebas de amplificación de ácidos nucleicos (NAATs)
La amplificación de ácidos nucleicos mediante diferentes métodos constituye una herramienta molecular importante, tanto en la investigación básica, como en el desarrollo de la medicina clínica y el diagnóstico de enfermedades infecciosas15.
Los métodos de diagnóstico estándares incluyen aislamiento de virus, detección de antígenos y serología, pero las principales limitaciones de estas técnicas incluyen tiempo de procesamiento prolongado, análisis subjetivo, baja sensibilidad y/o baja especificidad. El uso de técnicas de amplificación de ácidos nucleicos ha demostrado proveer un diagnóstico sensible de la infección por el virus de la influenza, incluso con la posibilidad de determinar el tipo de virus16. Una diversidad de exámenes, basados en ácidos nucleicos, están disponibles para el diagnóstico de infección viral por Influenza en humanos, estos incluyen: la transcripción reversa-PCR (RT- PCR), la secuenciación de nueva generación (NGS), ADN microarray, la técnica de amplificación isotérmica mediada por bucle (LAMP), entre otros10,15.
Los métodos moleculares tienen una gran ventaja sobre otros métodos de diagnóstico, entre ellas está la rapidez, ya que la mayoría de estos exámenes toman de 2 a 4 horas en completarse, demostrando alta sensibilidad y especificidad comparada con los exámenes basados en detección de antígenos10; demuestran una mayor sensibilidad a los métodos convencionales para la detección de virus poco viables, difíciles de aislar en cultivo celular o que están presentes en pequeñas cantidades; incrementando además, la capacidad para detectar virus respiratorios en muestras de pacientes adultos que, a diferencia de los niños, presentan una menor carga viral13. Otra de las ventajas de las técnicas moleculares es que pueden ser automatizadas en el laboratorio, reduciendo el costo del personal técnico, minimizando errores y ganando reproducibilidad13.
Dentro de las desventajas de los resultados de algunas pruebas moleculares pueden ser que no siempre están listas dentro de un periodo clínicamente relevante como para informar las decisiones de gestión clínica, ya que la detección del ARN viral de la Influenza por este medio molecular no siempre indica la viabilidad del virus o su continua replicación viral13. La RT-PCR y otras pruebas moleculares pueden no estar disponibles en todas las salas de emergencia o entornos ambulatorios, es posible que las muestras respiratorias tengan que enviarse a un laboratorio especializado, siendo, además, más costosos y complejos que otras pruebas de influenza. Por consiguiente, aunque la prueba puede arrojar resultados en horas, el tiempo real para recibir los resultados puede ser mucho mayor13,17. Algunos ensayos moleculares pueden no identificar de manera específica todos los subtipos de virus de influenza A que circulan actualmente, por lo que un resultado negativo de un subtipo de virus de influenza A no descarta la infección con otro subtipo de virus de influenza A17.
•RT-PCR
Se desarrollaron diferentes variantes de la RT-PCR para detectar al virus de la influenza, tales como RT-PCR multiplex que detecta virus A tipos H1 y H3 y virus tipo B, para discriminar virus de influenza de otros virus respiratorios; esta PCR multiplex es una modificación a la PCR, la cual permite utilizar múltiples pares de cebadores en la misma reacción para detectar simultáneamente diferentes blancos, ahorrando tiempo y dinero16,18. Existe, además, la RT-PCR en tiempo real (RRT-PCR por sus siglas en inglés), siendo rápida y proveyendo de resultados cuantitativos, para virus de influenza tipo A y los subtipos aviares H5 y H7; como utiliza sondas específicas a secuencias, se reducen las posibilidades de falsos positivos20.
Cultivo viral
El cultivo viral es un método tradicional para el diagnóstico de Influenza, fue considerado el método de referencia por su mayor sensibilidad, especificidad y reproducibilidad; actualmente se utiliza principalmente para vigilancia epidemiológica y no así para el manejo clínico13,21. El cultivo viral implica la inoculación de líneas celulares permisivas u óvulos embrionados con muestras infecciosas, comprende una propagación durante 7 a 10 días para controlar el desarrollo del efecto citopático y confirmación final de la infección por el virus de la influenza por tinción de anticuerpos específicos, hemadsorción con eritrocitos o microscopía de inmunofluorescencia10.
El tipo de muestra, la recolección, el transporte y la preparación de las muestras clínicas son factores muy importantes a considerar en el aislamiento de los virus en cultivo celular, especialmente en el caso de virus respiratorios que son particularmente lábiles13. La principal ventaja del cultivo celular es la confirmación de la viabilidad e infectividad del virus, información que no es posible obtener mediante los métodos de amplificación molecular y los métodos de detección de antígenos13.
Detección Inmunológica
Los métodos serológicos permiten confirmar una infección respiratoria aguda mediante la detección de anticuerpos específicos en suero frente a un determinado virus13. Los ensayos serológicos comúnmente utilizados para detectar respuestas de anticuerpos específicos del virus de la influenza incluyen: ensayo de inhibición de la hemaglutinación (HAI), ensayo de microneutralización o neutralización del virus (VN), hemólisis radial simple (SRH), ensayo de fijación del complemento, Ensayo de inmunoabsorción ligado a enzimas (ELISA) y Western blotting10.
Estos métodos no se consideran una herramienta de diagnóstico eficaz ni práctico, ya que requiere dos muestras de suero con una sincronización precisa y presenta un procesamiento de muestras prolongado23. Además, el resultado de la prueba no es fácilmente interpretable, con posibilidades de error en la interpretación para decisiones clínicas, por lo que no se recomienda esta técnica para el diagnóstico11. Su realización acostumbra a limitarse a estudios seroepidemiológicos y de seroprotección poblacional retrospectivos13.
Pruebas de diagnóstico rápido de la influenza (RIDTs)
Existen diversas pruebas para detectar al virus de la influenza, las más comunes se denominan “Pruebas de diagnóstico rápido de la influenza” (RIDTs, por sus siglas en inglés). Estos test comercialmente disponibles, son mayormente inmunoensayos que detectan los antígenos que estimulan una respuesta inmunitaria, usando anticuerpos monoclonales que se dirigen a la nucleoproteína viral y emplean inmunoensayo enzimático o inmunocromatografía11,17. El rendimiento de las RIDTs depende de la prevalencia de los virus de la Influenza que circula en la población y han mostrado alta especificidad (95-99%) para la detección de Influenza estacional17, estos permiten detectar y diferenciar los tipos de virus de influenza A y B, teniendo mayor sensibilidad para influenza tipo A (71%-99%) que para influenza tipo B (33%-100%), pero no identifican ni diferencian específicamente los subtipos de virus de influenza A21,23. Se ha demostrado que su rendimiento es mejor en niños en comparación con los adultos, potencialmente debido a mayores cargas virales y más tiempo de excreción viral en niños en comparación con adultos24. Aunque generan resultados entre 15 a 30 minutos, son fáciles de interpretar y su especificidad está entre el 90 a 95%, pero tienen muy baja sensibilidad en comparación al cultivo viral o a la PCR4,11,25.
Detección de antígenos mediante inmunofluorescencia
Hay diferentes métodos basados en la detección de antígenos para Influenza virus que, a pesar de presentar una menor sensibilidad y especificidad respecto de los métodos moleculares, permiten un diagnóstico más rápido y sencillo. Estos métodos se basan en la inmunocromatografía capilar, el enzimoinmunoanálisis de membrana o la Inmunofluorescencia (IF)13.
La detección del virus de la influenza por microscopía de inmunofluorescencia, puede ser mediante la prueba de “anticuerpo fluorescente directo” (DFA, por sus siglas en inglés) o prueba de “anticuerpo inmunofluorescente” (IFA, por sus siglas en inglés), siendo métodos muy útiles, a pesar del equipamiento e infraestructura extensos26. El método DFA implica el tratamiento de células epiteliales respiratorias con anticuerpos específicos directamente conjugados con un tinte fluorescente y una posterior aplicación con un conjugado de anticuerpo monoclonal en un portaobjetos soldado. Su sensibilidad y especificidad dependen de la presencia de un número adecuado de células infectadas, y pueden variar según el tipo de muestra. Esta es una prueba diagnóstica muy útil porque proporciona resultados rápidos y relativamente precisos, siendo una buena opción para confirmar los resultados de la prueba rápida11,13,26.
La técnica IFA implica la tinción de células secas y fijas con un anticuerpo monoclonal contra los virus respectivos y luego con un anticuerpo conjugado con inmunoglobulina de ratón, es decir, mediante la detección directa o indirecta de los antígenos virales mediante anticuerpos marcados con fluoresceína, examinando la preparación de la muestra bajo un microscopio de fluorescencia11,13,26. La especificidad de la prueba de detección de antígeno mediante IFA es alta, pero depende de la experiencia del profesional que la realiza. Su sensibilidad puede variar de un mínimo del 50 al 80% en comparación con las pruebas de amplificación de ácidos nucleicos. Además del poco tiempo requerido para la realización de la técnica y la rapidez en la generación de resultados, otra de las ventajas es el bajo costo de los reactivos. Existen otros métodos rápidos de detección de antígenos, basados en técnicas de inmunocromatográfica capilar y de enzimoinmunoanálisis de membrana, que tienen la ventaja adicional de ser de lectura visual sin necesidad de instrumental, no obstante, presentan una baja sensibilidad (10-75%) y especificidad (50-100%)6,11,13,27.
Conclusiones
La influenza es una enfermedad que compromete la salud de millones de personas y genera altos costos en atención médica. Después de la experiencia de la última pandemia por influenza A (H1N1 pmd09) que cobró la vida de miles de personas a nivel mundial, se vio necesaria la optimización y actualización de los métodos de diagnóstico para esta enfermedad que detecten, además, a los nuevos subtipos de influenza circulantes, de manera que se puedan evitar complicaciones asociadas, tratamientos inadecuados y gastos hospitalarios innecesarios.
Aunque el diagnóstico de laboratorio para influenza sigue presentando limitaciones, los avances tecnológicos permiten el desarrollo y mejora de las técnicas para la detección del virus, lo que genera más alternativas de diagnóstico útiles para los profesionales en salud, proporcionando herramientas para un mejor manejo del paciente. Sin embargo, es importante considerar que los resultados de laboratorio siempre deben interpretarse junto con la historia clínica del paciente y los reportes epidemiológicos regionales, además es recomendable realizar más de una prueba para confirmar el diagnóstico.
A pesar de las alternativas de métodos de laboratorio disponibles, es necesario analizar las ventajas y desventajas de cada técnica para su implementación, además de tomar en cuenta el comportamiento del virus y la aparición de nuevos subtipos para los cuales las pruebas disponibles no son sensibles o específicas. Asimismo, en nuestro medio se tiene que considerar limitantes en cuanto a costos, infraestructura, experticia del personal de laboratorio, entre otros, que podrían restringir su aplicación.
Referencias bibliográficas
1. Monto A, Gravenstein S, Elliott M. Clinical Signs and Symptoms Predicting Influenza Infection. Arch Intern Med. 2000. Vol. 160: 3243-3247.
2. Solórzano-Santos F, Miranda-Novales Ma. G. Influenza. Bol Med Hosp Infant Mex. 2009. Vol. 66, No 5: 461-473.
3. Peteranderl C, Herold S, Schmoldt C. Human Influenza Virus Infections. Seminars in Respiratory and Critical Care Medicine. 2016; Vol. 37, No 04: 487-500.
4. NCIRD (Centers for Disease Control and Prevention, National Center for Immunization and Respiratory Diseases). Understanding Influenza Viruses. [Internet]. [citado 30 de julio de 2019]. Disponible en: https://www.cdc.gov/flu/about/viruses/index.htm
5. Rivera J, Neira M, Sarmiento L, Parra E, Caldas ML. Virus de la influenza. Biomédica. 2016. Vol. 36:174-175.
6. Petric M, Comanor L, Petti CA. Role of the laboratory in diagnosis of influenza during seasonal epidemics and potential pandemics. J Infect Dis. 2006. Vol. 194 (Suppl 2): S98–110.
8. OPS (Organización Panamericana de la Salud). Informe de situación de Influenza. [Internet]. [citado 01 de agosto de 2019]. Disponible en: https://www.paho.org
9. Martínez M, Piñón A, Acosta B, Valdés O. et al. Introducción de nuevos ensayos de reacción en cadena de la polimerasa en tiempo real para el diagnóstico y vigilancia de virus respiratorios. Rev Cubana Med Trop. 2018. Vol. 70 (3): 1.
10. Vemula S, Zhao J, Liu J, Wang X, Biswas S, Hewlett I. Current Approaches for Diagnosis of Influenza Virus Infections in Humans. Viruses. 2016. Vol. 8 (4), 96: 1-15.
11. Kim DK, Poudel B. Tools to Detect Influenza Virus. Yonsei Med J. 2013. Vol. 54, Nº 3:560-566.
12. FDA (Food & Drug Administration). 2019. Nucleic Acid Based Tests. [Internet]. [citado 20 de agosto de 2019]. Disponible en: https://www.fda.gov/medical-devices/vitro-diagnostics/nucleic-acid-based-tests
13. Antón A, Pumarola T. Diagnóstico microbiológico de las infecciones virales respiratorias en el paciente adulto. Enferm Infecc Microbiol Clin. 2014. Vol. 32 (Supl 1): 51-56.
14. WHO (World Health Organization). WHO information for molecular diagnosis of influenza virus in humans-update. Bulletin of the World Health Organization. 2011. 1-38.
15. Fakruddin M, Mannan K, Hossain M, Islam S, Mazumdar R, Chowdhury A, Chowdhury M. Nucleic acid amplification: Alternative methods of polymerase chain reaction. Journal of Pharmacy and Bioallied Sciences. 2013.Vol. 5, Nº 4: 245-252.
16. Herrmann B, Larsson C, Zweygberg BW. Simultaneous Detection and Typing of Influenza Viruses A and B by a Nested Reverse Transcription-PCR: Comparison to Virus Isolation and Antigen Detection by Immunofluorescence and Optical Immunoassay (FLU OIA). Journal of Clinical Microbiology. 2001. Vol. 39: 134-138.
18. Valassina M, Cuppone AM, Cusi MG, Valensin PE. Rapid detection of different RNA respiratory virus species by multiplex RT-PCR: application to clinical specimens. Clinical and Diagnostic Virology. 1996. Vol. 8: 227-232.
19. Pachucki C, Khurshid MA, Nawrocki J. Utility of Reverse Transcriptase PCR for Rapid Diagnosis of Influenza A Virus Infection and Detection of Amantadine-Resistant Influenza A Virus Isolates. Journal of Clinical Microbiology. 2004. Vol. 42: 2796–2798.
20. Spackman E, Senne D, Myers TJ, Bulaga L, Garber L, Perdue, M, et al. Development of a Real-Time Reverse Transcriptase PCR Assay for Type A Influenza Virus and the Avian H5 and H7 Hemagglutinin Subtypes. Journal of Clinical Microbiology. 2002. Vol. 40: 3256–3260.
21. Prado H, Prado A. Evidencias para el diagnóstico y tratamiento de influenza en adultos. Aten Fam. 2018. Vol. 25(3): 118-122.
22. Cox NJ, Subbarao K. Influenza. Lancet. 1999. Vol. 354: 1277-1282.
23. Centers for Disease Control and Prevention, National Center for Immunization and Respiratory Diseases (CDC-NCIRD). Rapid Diagnostic Testing for Influenza: Information for Clinical Laboratory Directors. [Internet]. [citado 18 de agosto de 2019]. Disponible en: https://www.cdc.gov/flu/professionals/diagnosis/rapidlab.htm
24. Cruz A, Demmler-Harrison GJ, Caviness C, Buffone GJ, Revell P. Performance of a Rapid Influenza Test in Children During the H1N1 2009 Influenza A Outbreak. Pediatrics 2010. Vol. 125 (3): e645-650.
25. CDC: Centers for Disease Control and Prevention. Role of Laboratory Diagnosis of Influenza. [Internet]. [citado 06 de agosto de 2019]. Disponible en: http://www.cdc.gov/flu/professionals/diagnosis/labrole.htm
26. Gaydos C. What Is the Role of Newer Molecular Tests in the Management of CAP?. Infectious Disease Clinics of North America. 2013. Vol. 27(1): 49-69.