INTRODUCCIÓN
La diversidad de los recursos fitogenéticos es esencial para la seguridad alimentaria global, ya que incluye la variabilidad genética de las plantas utilizadas en la agricultura y la alimentación. Estos recursos permiten adaptar los cultivos a diversas condiciones climáticas y resistir plagas y enfermedades, lo que resulta en un aumento de la productividad agrícola. Sin embargo, esta diversidad enfrenta amenazas significativas, como el cambio climático y la pérdida de hábitats naturales. Por ello, es crucial implementar estrategias de conservación y uso sostenible para garantizar su disponibilidad futura y proteger la biodiversidad del planeta. La conservación de estos recursos no solo apoya el desarrollo agrícola sostenible, sino que también es vital para enfrentar los desafíos alimentarios actuales y futuros.
En este sentido, la papa (Solanum sp.) es un cultivo esencial para la seguridad alimentaria a nivel mundial, destacando especialmente en regiones andinas como Huancavelica, donde las variedades nativas constituyen una parte fundamental del sustento alimenticio y cultural de las comunidades locales (1). La cuales son fruto de siglos de interacción entre la cultura campesina y el entorno agroecológico, son un reservorio genético invaluable, crucial para enfrentar los desafíos que plantean los cambios climáticos y la creciente demanda de alimentos (2,3).
En relación, a la caracterización morfológica de las papas nativas de Huancavelica es fundamental para su correcta identificación y conservación. Según Gómez (4), es esencial documentar los rasgos fenotípicos básicos, ya que esto complementa los análisis moleculares y mejora el manejo sostenible de estos valiosos recursos. En Huancavelica, se cultivan más de 200 variedades de papas nativas, cada una con características únicas que reflejan la rica biodiversidad de la región. Estas variedades no solo son importantes para la alimentación local, sino que también están siendo industrializadas para agregar valor a través de productos como chips de colores y harinas. La preservación de estas papas es crucial para mantener la herencia cultural y agrícola del Perú, así como para enfrentar los desafíos del cambio climático y la seguridad alimentaria.
Por su lado, Huancavelica, como parte del centro de origen de la papa, alberga una notable diversidad genética que incluye variedades aún no caracterizadas ni inventariadas en bancos de germoplasma (1,5). Investigaciones previas, como la realizada por Bernardo (6) en Huánuco, han demostrado cómo las características genéticas y la distribución espacial de las papas nativas están influenciadas por factores geográficos y prácticas agrícolas tradicionales.
La diversidad genética no solo es clave para el mejoramiento genético y la resistencia a condiciones abióticas extremas, sino que también es vital para garantizar la seguridad alimentaria mediante de la conservación y uso sostenible de los recursos fitogenéticos (7,8). Herramientas moleculares, como los marcadores microsatélites (SSR), ha sido fundamentales para caracterizar y evaluar la diversidad genética. En esta dirección, Ashkenazi et al. (9) desarrollaron y validaron marcadores SSR específicos para papa, demostrando su utilidad en estudios de diversidad genética, análisis filogenéticos y huellas genéticas (fingerprinting), lo que sienta las bases para su aplicación en investigaciones como esta. Asimismo, Soto (10) reportó que el uso de SSR ha permitido identificar patrones significativos de variabilidad genética en papas nativas de diversas regiones andinas del Perú.
Estos hallazgos resaltan la importancia de preservar tanto la diversidad genética como los conocimientos tradicionales asociados a su manejo, en concordancia con los objetivos de este trabajo. No obstante, Huancavelica también se encuentra entre las regiones más afectadas por la pobreza en el Perú, según el INEI (11), esta situación incrementa la vulnerabilidad de las comunidades agrícolas y limita los recursos disponibles para la conservación y uso sostenible de las papas nativas. Por lo tanto, es crucial implementar estrategias integrales que combinen la conservación genética con iniciativas de desarrollo socioeconómico.
Este enfoque permite identificar haplotipos y evaluar la estructuración genética dentro y entre comunidades, aportando información fundamental para el diseño de estrategias de conservación y mejoramiento genético orientadas a fortalecer la seguridad alimentaria en estas regiones y en otros contextos similares (12,13). Por consiguiente, el presente estudio tiene como objetivo analizar la diversidad genética de papas nativas cultivadas en tres distritos: Paucará, Rosario, Anta de la región de Huancavelica - mediante el uso de marcadores moleculares microsatélites (SSR).
MATERIALES Y MÉTODOS
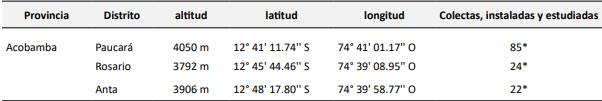
La investigación se desarrolló bajo en enfoque cuantitativo, alcance descriptivo y diseño tranversal. La cual se materializó en tres comunidades de la región de Huancavelica, Perú: Paucará, Rosario, Anta Tabla 1, seleccionadas por su alta diversidad de papas nativas y el conocimiento ancestral de sus agricultores.
* Se logró extraer ADN en todos los cultivares instalados, no se tuvo ninguna pérdida de cultivo.
Por otra parte, se recolectaron muestras de 131 cultivares de papa nativa en los tres distritos seleccionadas, ubicadas a altitudes entre 3,792 y 4,050 msnm. Cada muestra fue identificada con su nombre común y asociada a sus custodios. Las ubicaciones geográficas de las comunidades fueron registradas con un GPS de alta precisión, y la información fue sistematizada para generar una base de datos georreferenciada. Este enfoque sigue metodologías similares a las reportadas por Bernardo (6) y Soto (10), quienes destacaron la importancia de combinar datos geográficos con características genéticas mediante el uso de marcadores SSR para analizar la diversidad genética de poblaciones de papa nativa, lo que permite comprender su relación con las prácticas agrícolas locales.
En relación a la extracción de ADN se realizó siguiendo el protocolo CTAB modificado (14). Se pesaron 220 mg de tejido foliar fresco por muestra y se procesaron en tubos de 2 ml, utilizando tampón CTAB al 2 %, β-mercaptoetanol y una esfera cerámica para homogeneización en un equipo Fastprep 5G. El ADN extraído fue purificado mediante tratamiento con ARNasa y su integridad fue evaluada en geles de agarosa al 1 %, teñidos con GelRed. La cuantificación se realizó utilizando un espectrofotómetro Epoch a longitudes de onda de 230, 260 y 280 nm, y las muestras se diluyeron a una concentración final de 5 ng/µl.
En cuanto al genotipado molecular, se utilizaron 12 marcadores microsatélites nucleares (SSR) previamente validados para Solanum sp. (13). Los SSR han demostrado ser herramientas altamente efectivas para analizar la diversidad genética y establecer relaciones filogenéticas en papa, como lo reportaron Ashkenazi et al. (9), quienes desarrollaron y aplicaron estos marcadores en estudios de caracterización genética. Las reacciones de PCR se realizaron en un volumen final de 10 µl, empleando 5 µl de mezcla maestra (Master Mix) y 5 µl de ADN diluido. Los programas de amplificación se optimizaron para cada marcador, considerando las temperaturas de alineamiento específicas. Los productos de PCR se analizaron mediante electroforesis en geles de poliacrilamida al 6 %, teñidos con nitrato de plata para la visualización de bandas.
Además, los análisis descritos fueron realizados con los instrumentos y equipos siguientes: Espectrofotómetro Epoch (BioTek Instruments), Equipo Fastprep 5G (MP Biomedicals), Termociclador para PCR, Software NTSYSpc 2.2 y Arlequin 3.5.2.2, Electroforesis para Gel de agarosa y poliacrilamida, teñidos con GelRed y nitrato de plata, respectivamente.
Por otro lado, para realizar el análisis de los datos moleculares los alelos obtenidos fueron registrados en una matriz binaria (presencia = 1, ausencia = 0) y procesados en los softwares NTSYSpc 2.2 y Arlequin 3.5.2.2. Se calculó la diversidad genética mediante índices como el número de alelos por locus, la heterocigosidad promedio y el índice de fijación (Fst). La variación genética entre y dentro de comunidades fue analizada mediante un Análisis de Varianza Molecular (AMOVA). Asimismo, se generaron dendrogramas para visualizar la estructura genética de las muestras utilizando el coeficiente de similitud de Jaccard.
En este sentido, los resultados fueron validados mediante la prueba de Mantel, confirmando la correlación entre matrices genéticas y geográficas. Para garantizar la calidad de los resultados, se incluyeron controles positivos y negativos en cada etapa del análisis, y se replicaron los experimentos en un 20 % de las muestras. En este contexto, es preciso señalar que el procesamiento y análisis final de los datos se realizó en las instalaciones de la Universidad Nacional de Huancavelica entre julio de 2020 y marzo de 2023. Los resultados fueron interpretados en relación con estudios previos sobre la diversidad genética de papas nativas en los Andes, integrando los hallazgos con las necesidades de conservación y mejoramiento genético.
RESULTADOS Y DISCUSIÓN
Los resultados de la investigación sobre la diversidad genética de las papas nativas en Huancavelica proporcionan una visión integral de la variabilidad genética presente en esta región. Se logró identificar haplotipos únicos y evaluar la estructura genética de tres distritos específicos: Paucará, Rosario, Anta. Los resultados obtenidos revelan no solo la riqueza genética de estas papas, sino también la existencia de un flujo genético activo entre los distritos.
En este sentido, los marcadores moleculares microsatélites “SSR”, permitieron analizar la estructura y variabilidad genética de papa nativa y accedió identificar los haplotipos o perfil genético distintivo de cada cultivar en determinadas regiones del ADN. A partir del análisis de diversidad genética descritos se analizaron 131 cultivares de papa nativa. En este sentido, mediante el uso de 12 marcadores microsatélites (SSR), se identificaron un total de 116 alelos distribuidos en los 12 cromosomas estudiados. Además, se determinaron 51 haplotipos únicos, con la siguiente distribución: 45 en Paucará, 20 en Rosario y 16 en Anta. El 61,1 % de las muestras presentó duplicación genética, indicando la coexistencia de genotipos redundantes.
Por otra parte, en la tabla 2 se presentan los loci polimóficos y los niveles de heterocigosidad, resultando que de los 116 loci evaluados, siendo polimóficos 99, 80 y 58 en Paucará, Rosario y Anta, respectivamente. La heterocigosidad promedio fue mayor en Anta (0,33), seguida de Rosario (0,26) y Paucará (0,21). Estos valores reflejan la presencia de una alta tasa de multi-locus y diversidad genética en las papas nativas conservadas por los agricultores.
Además, se identificaron un total de 51 haplotipos únicos: 45 en Paucará, 20 en Rosario y 16 en Anta, respectivamente con un 61,1 % de duplicados Tabla 2. Estos haplotipos reflejan la presencia o ausencia de marcadores moleculares SSR específicos en regiones del ADN, ubicados en los cromosomas de Solanum sp. Por otra parte, los resultados de la prueba de Mantel validaron la coherencia de los datos genéticos, confirmando una correlación significativa entre las matrices genéticas y geográficas (p = 0,001).
Tabla 2 Análisis del Correlación, t-test Mantel y diversidad molecular.
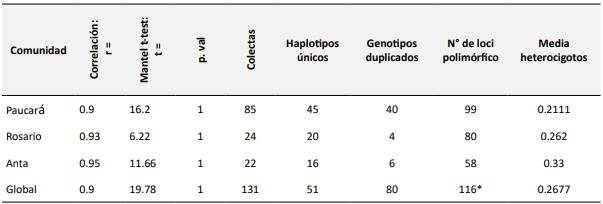
* Se detectó 116 loci, para fines de análisis molecular se consideró como haplotipos.
Según se observa en la Tabla 3, estos haplotipos únicos reflejan la presencia o ausencia de marcadores moleculares SSR (repeticiones cortas de ADN) en las regiones del ADN de los cromosomas de Solanum sp. La identificación de estos haplotipos es crucial para comprender la diversidad genética y las características específicas de los cultivares analizados, lo que puede tener implicaciones significativas en la conservación y mejora genética de estas especies. La información detallada sobre la presencia de nucleótidos en las diversas regiones del ADN se presenta en la tabla correspondiente.
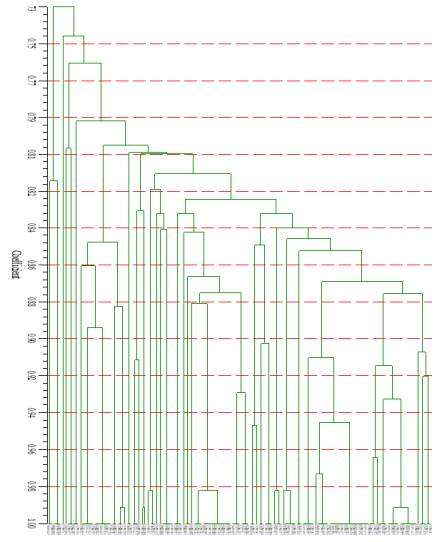
El análisis del dendográma Figura 1, que se fundamenta en el coeficiente de similitud genética, mostró una notable correlación entre los genotipos estudiados. Los coeficientes de similitud variaron entre el 90 % y el 95 %, lo que indica una alta homogeneidad genética entre los diferentes cultivares analizados. Esta estrecha relación sugiere que los genotipos comparten características genéticas significativas, lo que puede ser crucial para futuras investigaciones sobre la diversidad genética y la selección de cultivares. Este tipo de análisis es fundamental para comprender la estructura genética de las poblaciones y para guiar estrategias de conservación y mejora genética en Solanum sp.
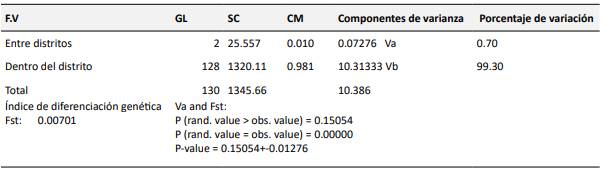
En relación a la estructura genética y variación dentro y entre comunidades, el análisis de varianza molecular presente en la Tabla 4, revela que la mayor parte de la variación genética se encuentra dentro de los distritos analizados, con un 99.30% del total, mientras que solo el 0.70% se atribuye a diferencias entre comunidades. Esto indica que la diversidad genética es predominantemente intra-comunitaria. El índice de fijación (FST) es bajo, con un valor de 0.00701, sugiriendo una escasa diferenciación genética entre los distritos. Además, el valor p asociado a la comparación de la variación observada y aleatoria es de 0.15054, lo que indica que no hay una diferencia significativa en la varianza entre distritos. Estos resultados destacan la importancia de la variabilidad genética dentro de las comunidades en el contexto estudiado.
El índice de fijación (Fst = 0,07 %) confirma esta baja diferenciación genética, indicando la presencia de individuos genéticamente similares entre distritos, pero con diversidad significativa dentro de ellas Figura 2.
Los hallazgos subrayan la importancia de las comunidades de Paucará, Rosario, Anta como centros de conservación in situ de la agrobiodiversidad de papas nativas. La variabilidad genética identificada refuerza la necesidad de implementar estrategias de conservación que integren programas de mejoramiento genético y la valorización de los conocimientos tradicionales de los agricultores custodios. Estos resultados demuestran que la región de Huancavelica es un centro clave de diversidad genética de papas nativas, con un alto potencial para contribuir a la conservación de agroecosistemas andinos y a la seguridad alimentaria.
Discusión
La diversidad genética de las papas nativas representa un recurso estratégico fundamental para garantizar la seguridad alimentaria, especialmente en regiones andinas como Huancavelica. Este estudio proporciona resultados que subrayan la importancia de los agroecosistemas tradicionales, los cuales actúan como reservorios valiosos de variabilidad genética. Esta variabilidad es crucial para el desarrollo de cultivos que puedan adaptarse a las condiciones agroecológicas cambiantes y a los desafíos que plantea el cambio climático, como la variabilidad en las precipitaciones y las temperaturas extremas. Además, la conservación y el uso sostenible de esta diversidad genética no solo contribuyen a la resiliencia de los sistemas agrícolas, sino que también promueven la sostenibilidad de las comunidades locales, asegurando así su capacidad para enfrentar futuros retos alimentarios y ambientales (2,3).
En este sentido, en el presente estudio se identificaron una cifra menor de haplotipos únicos que la reportada por De Haan (3), quien utilizó 18 marcadores SSR polimórficos para analizar 989 accesiones de papa en las zonas norte, centro y sur de la región Huancavelica, identificando 406 cultivares únicos (3,15). Por su parte, Montalvo (12), caracterizó 425 entradas de papa nativa con 12 SSR en la zona centro de Huancavelica, encontrando 198 genotipos únicos con un coeficiente de similitud de uno y un 50,1 % de duplicados. Estas diferencias pueden atribuirse a factores como la cantidad y diversidad de cultivares disponibles en las comunidades estudiadas, la ubicación geográfica, el grado de urbanización, el tamaño de las muestras, las metodologías empleadas, el tiempo transcurrido entre los estudios, y procesos como el desplazamiento de cultivos, pérdida de variedades o erosión genética. Estos resultados subrayan la importancia de la conservación y caracterización continua de los recursos genéticos en la región.
Por otro lado, el hallazgo de un número significativo de haplotipos únicos en este estudio es consistente con investigaciones previas que destacan la alta variabilidad genética presente dentro de las comunidades andinas. Estos resultados subrayan la capacidad de los agricultores locales para gestionar y conservar esta diversidad a través de prácticas tradicionales de cultivo, que han sido fundamentales para la sostenibilidad agrícola en la región. Además, la baja estructuración genética observada entre las comunidades, con un valor Fst del 0.07%, sugiere un flujo genético activo. Este fenómeno puede estar influenciado por el intercambio de semillas, una práctica común en las regiones andinas que no solo fomenta la diversidad genética, sino que también fortalece la resiliencia de los cultivos ante cambios ambientales. Estos hallazgos resaltan la importancia de las estrategias locales en la conservación de recursos genéticos.
En este sentido, la identificación de loci polimórficos y haplotipos únicos en este estudio pone de manifiesto el gran potencial que poseen estos genotipos para ser utilizados en programas de mejoramiento genético, especialmente aquellos orientados hacia la resistencia a plagas, enfermedades y estrés abiótico. Estos atributos son cruciales para abordar los desafíos que plantea el cambio climático, así como la erosión genética que afecta a muchos cultivos tradicionales. Al incorporar esta diversidad genética en los programas de mejora, se puede garantizar la sostenibilidad de los sistemas agrícolas en las comunidades locales, lo que a su vez contribuye significativamente a la seguridad alimentaria regional. De este modo, el uso estratégico de estos genotipos no solo fortalece la producción agrícola, sino que también promueve la resiliencia de los distritos ante un futuro incierto, asegurando su capacidad para adaptarse a condiciones cambiantes (8,15).
Además, los resultados obtenidos en este estudio destacan la urgente necesidad de implementar estrategias efectivas de conservación tanto in situ como ex situ para salvaguardar esta valiosa riqueza genética. Huancavelica, reconocido como uno de los centros de diversidad genética de papas nativas, merece atención prioritaria en el diseño de políticas que no solo se enfoquen en la conservación de la agrobiodiversidad, sino que también integren estos esfuerzos con iniciativas destinadas a mejorar la calidad de vida de las comunidades agrícolas. Es fundamental que las políticas consideren la participación activa de los agricultores locales, quienes son los guardianes del conocimiento tradicional y de la diversidad genética. De esta manera, se puede asegurar un enfoque sostenible que beneficie tanto a la conservación del patrimonio agrícola como al bienestar socioeconómico de las comunidades (7,2).
Por último, este estudio aporta evidencia sólida para respaldar la relevancia de las papas nativas en la seguridad alimentaria de las regiones andinas, no solo por su aporte a la diversificación de la dieta, sino también por su papel como una fuente clave de genes para enfrentar las necesidades futuras de la agricultura sostenible (1,4,16). Estos resultados deben ser considerados en la planificación de programas nacionales e internacionales que promuevan la conservación y uso sostenible de los recursos genéticos.
CONCLUSIONES
El análisis de la diversidad genética de papas nativas cultivadas en tres distritos de Huancavelica -Paucará, Rosario, Anta- identificó 51 haplotipos únicos y una alta variabilidad genética dentro del distrito (99.30 %). Estos resultados destacan a Huancavelica como uno de los principales centros de conservación de papas nativas, lo que subraya la importancia de su diversidad genética como recurso clave para programas de mejoramiento genético y estrategias de seguridad alimentaria.
La riqueza genética documentada en este estudio es esencial para enfrentar desafíos como el cambio climático, la aparición de nuevas plagas y enfermedades, y la adaptación a condiciones agroecológicas extremas. Los haplotipos identificados representan una fuente de genes valiosos que pueden ser utilizados en el desarrollo de variedades resistentes y productivas, contribuyendo directamente a la seguridad alimentaria de las regiones andinas y más allá.
La baja estructuración genética entre comunidades (Fst = 0,07 %) indica la existencia de un flujo genético activo, posiblemente facilitado por prácticas culturales como el intercambio de semillas. Esto resalta la necesidad de estrategias de conservación in situ que protejan tanto los agroecosistemas como los conocimientos tradicionales de los agricultores, esenciales para mantener esta diversidad genética.
Este estudio aporta evidencia para diseñar políticas integrales que promuevan la conservación y uso sostenible de la agrobiodiversidad en Huancavelica. Integrar esta riqueza genética en programas nacionales e internacionales de seguridad alimentaria y cambio climático es fundamental para garantizar su preservación y aprovechamiento.
Los agricultores de Huancavelica son custodios de una invaluable agrobiodiversidad, cuya preservación y uso sostenible deben ser reconocidos y fortalecidos mediante capacitación y acceso a tecnologías modernas, como el uso de marcadores moleculares, para mejorar la identificación y manejo de los recursos genéticos.