INTRODUCCIÓN
La enfermedad de Chagas es una afección parasitaria sistémica causada por el protozoo Trypanosoma cruzi y transmitida por el insecto heteróptero de la familia Reduviidae, Triatoma infestans. Es un problema epidemiológico significativo debido a su alta prevalencia en poblaciones pobres, la dificultad de control del vector y las graves complicaciones cardíacas y digestivas que puede causar. Aunque es endémica en 21 países de las Américas, la movilidad poblacional ha llevado a su detección en 44 países, incluidos Canadá, Estados Unidos, varios países europeos, del Pacífico Occidental, África y el Mediterráneo Oriental (OMS, 2024).
En Bolivia, la enfermedad de Chagas está presente en la Amazonia, los Valles Interandinos y el Chaco Boliviano. El país tiene la mayor prevalencia mundial de esta enfermedad, con más de 600,000 personas infectadas según la Coalición Chagas. Anualmente, se registran más de 8,000 nuevos casos debido a la picadura de la vinchuca, que transmite el parásito T. cruzi (Ministerio de Salud y Deportes de Bolivia, 2016).
El departamento de La Paz fue uno de los primeros en recibir la certificación de la OMS por interrumpir la transmisión vectorial de la enfermedad de Chagas. Sin embargo, investigaciones recientes muestran que la vinchuca (T. infestans), el principal vector, ha migrado y adaptado su comportamiento a diferentes ecotopos, posiblemente debido al cambio climático o a necesidades alimenticias, especialmente en el Municipio de Mecapaca (Zapata y col., 2019).
El presente estudio se basa en los resultados del proyecto IDH 3031 del Laboratorio de Genética Molecular del Instituto SELADIS, cuyo objetivo fue determinar la dispersión geográfica de las poblaciones silvestres y domésticas de T. infestans en el municipio de Mecapaca y los resultados confirmaron aquello. En este estudio se ha visto que la identificación de sangre humana en los contenidos gástricos de los especímenes de T. infestans guardados en el banco de material biológico del Laboratorio de Genética Molecular del Instituto SELADIS, sería crucial para comprender mejor sus patrones de alimentación y su implicancia en la transmisión de la enfermedad de Chagas.
El análisis de Short Tándem Repeats (STRs) utiliza la reacción en cadena de la polimerasa (PCR) combinada con la técnica de electroforesis capilar. Este enfoque permite una identificación humana precisa y es altamente eficaz en procesos de filiación, alcanzando una sensibilidad superior al 99,9 % (Butler, 2005).
En el presente estudio, se empleó el análisis de secuencias de STRs para la búsqueda de un perfil genético humano mediante la amplificación de 24 marcadores genéticos. De estos, 21 corresponden a marcadores genéticos de ADN nuclear, uno es un marcador de sexo (amelogenina) y dos son marcadores del cromosoma Y. El análisis se realizó en el contenido gástrico de T. infestans capturados en áreas periurbanas de la comunidad de Huajchilla. Los resultados obtenidos proporcionarán una comprensión más profunda de la ecología de estos vectores, aportando información esencial para diseñar estrategias de control y prevención de la enfermedad de Chagas. La creciente importancia de las poblaciones silvestres de T. infestans en la transmisión del parásito T. cruzi resalta la necesidad de abordar tanto los vectores domésticos como los silvestres, especialmente en áreas rurales y periurbanas donde la presencia de estos vectores no era tradicionalmente esperada. Esto presenta nuevos desafíos para el manejo efectivo de la enfermedad.
METODOLOGÍA
El estudio es de tipo observacional y descriptivo con análisis biológicos, se centró en la identificación de ADN humano en los contenidos gástricos de T. infestans mediante el análisis de secuencias STRs. Las secuencias fueron amplificadas por PCR y separadas por electroforesis capilar para obtener los fragmentos de ADN. Posteriormente, se utilizó el software GeneMapper versión 1.0 para generar los electroferogramas y traducirlos en perfiles genéticos. Los datos se obtuvieron del proyecto IDH 3031 del Laboratorio de Genética Molecular del Instituto SELADIS.
Preparación de muestras: Los contenidos gástricos de los especímenes adultos se encontraban almacenados en el banco de material biológico del Laboratorio de Genética Molecular del Instituto SELADIS. Para realizar el análisis, se recuperaron las muestras preservadas a -20 °C, garantizando así la estabilidad de las biomoléculas presentes. Posteriormente, se descongelaron las muestras en condiciones controladas para evitar la degradación y proceder con la extracción del material genético.
Extracción de ADN: Para la extracción de ADN de las muestras de contenido gástrico recuperadas, se empleó el kit comercial Wizard® Genomic DNA Purification Kit (PROMEGA). El procedimiento inició con la lisis celular, en la cual se añadió un buffer de lisis para romper las células y liberar el material genético. Posteriormente, se realizó la eliminación de proteínas mediante precipitación con una solución salina, lo que permitió separar las proteínas del ADN. El ADN genómico de alto peso molecular se concentró utilizando una columna de purificación. Finalmente, el ADN se precipitó con isopropanol y se lavó con etanol para eliminar impurezas. El ADN purificado mediante este sistema resultó ser el más adecuado para los análisis posteriores.
Cuantificación del ADN: Se utilizó el método fluorométrico para cuantificar el ADN purificado, utilizando el equipo Qubit y el kit de cuantificación ADN HS de la línea comercial Invitrogen, siguiendo las instrucciones del fabricante. Las muestras deben contener una concentración de 1 ng/ul para poder realizar la amplificación del ADN extraído.
Amplificación de ADN: Considerando que el material genético fue extraído del contenido intestinal, era posible la presencia tanto de ADN del propio T. infestans como del parásito T. cruzi, además de otros posibles contaminantes genéticos provenientes de los restos de alimentos ingeridos o de otros microorganismos presentes en el intestino. Para la amplificación del ADN de interés, se empleó la técnica de PCR Multiplex utilizando el kit comercial GlobalFiler™ (Applied Biosystems). Este kit permitió la amplificación de 24 marcadores genéticos de origen humano, incluyendo 21 marcadores STRs (Short Tándem Repeats) en los loci: D3S1358, vWA, D16S539, CSF1PO, TPOX, D8S1179, D21S11, D18S51, D2S441, D19S433, TH01, FGA, D22S1045, D5S818, D13S317, D7S820, SE33, D10S1248, D1S1656, D12S391 y D2S1338, además de un marcador STR del cromosoma Y (DYS391), un marcador de inserción/deleción del cromosoma Y (Indel) y un marcador de sexo, la amelogenina.
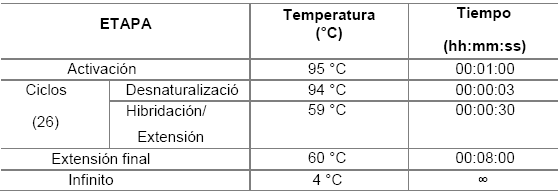
El protocolo de amplificación se llevó a cabo en un termociclador Veriti de la línea comercial Applied Biosystems. Este consistió en 26 ciclos de la siguiente manera: un ciclo inicial de activación a 95 °C durante un minuto, seguido de 25 ciclos con desnaturalización a 94 °C durante 3 segundos, alineamiento a 59 °C durante 30 segundos, y una extensión final a 60 °C durante 8 minutos. Finalmente, el producto amplificado se mantuvo a 4 °C hasta su posterior análisis. (Tabla 1).
Tabla 1 Protocolo de Amplificación por PCR Multiplex utilizando el Sistema de Marcadores GlobalFiler™ de Applied Biosystems
Electroforesis Capilar: Se procedió a realizar la dilución de Productos de PCR en una mezcla de formamida (Hi-Di) y el marcador de tamaño GeneScan™ Liz® 600 (Applied Biosystems). Posteriormente se procedió a desnaturalizar las muestras a 95°C durante 3 minutos y enfriar sobre hielo. Para la separación de los fragmentos de ADN obtenidos, las muestras amplificadas se cargaron en un analizador genético ABI 3500de Applied Biosystems. Los productos de PCR fueron separados mediante electroforesis capilar bajo las siguientes condiciones: se utilizó un capilar de 36 cm de longitud, con un voltaje de 1.2 kV y una temperatura de 60 °C durante un tiempo de 30 minutos. Se empleó la matriz Dye Set J6, para las calibraciones espaciales y espectrales que es compatible y adecuada para el kit GlobalFiler™ para la lectura de 6 fluoroforos.
Análisis de Datos: Los datos obtenidos se analizaron con el software GeneMapper™ versión 1.0 de Applied Biosystems, el cual permitió obtener los perfiles genéticos de las muestras.
RESULTADOS Y DISCUSIONES
Se analizaron seis muestras, de las cuales cinco no proporcionaron material genético adecuado para el análisis, lo que sugiere la ausencia de ADN humano detectable. Esto podría indicar que las vinchucas que proporcionaron estas muestras no se alimentaron de sangre humana. En la muestra restante, se obtuvo un perfil genético parcial correspondiente a 14 marcadores, identificándose como perteneciente a un individuo de sexo femenino (tabla 2 y figura 1).
Tabla 2 Tabla de alelos de los marcadores genéticos STRs (Short Tándem Repeats)
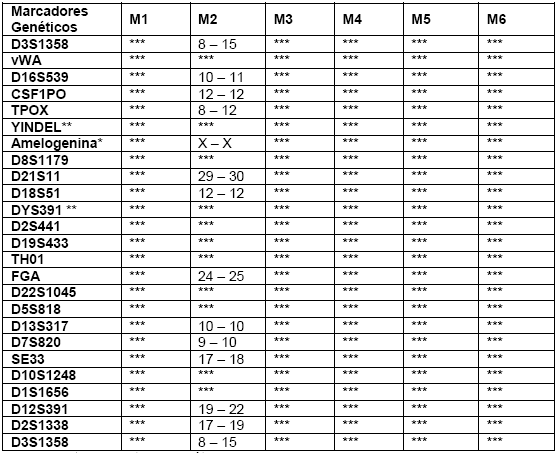
M = Muestra; ***Material genético analizable; """Marcadores "Y" STRs; *Amelogenina: marcador del sexo; X - X = Sexo femenino; X - Y = Sexo masculino
En la muestra M2 se observa un perfil genético parcial donde se identifica la presencia de alelos específicos en 14 loci: D3S1358 (15-15), D16S539 (10-11), CSF1PO (12-12), y D21S11 (29-30), entre otros. La presencia de X-X en el marcador Amelogenina indica que el ADN proviene de una persona de sexo femenino. Sin embargo, en 8 loci no se encontró material genético analizable
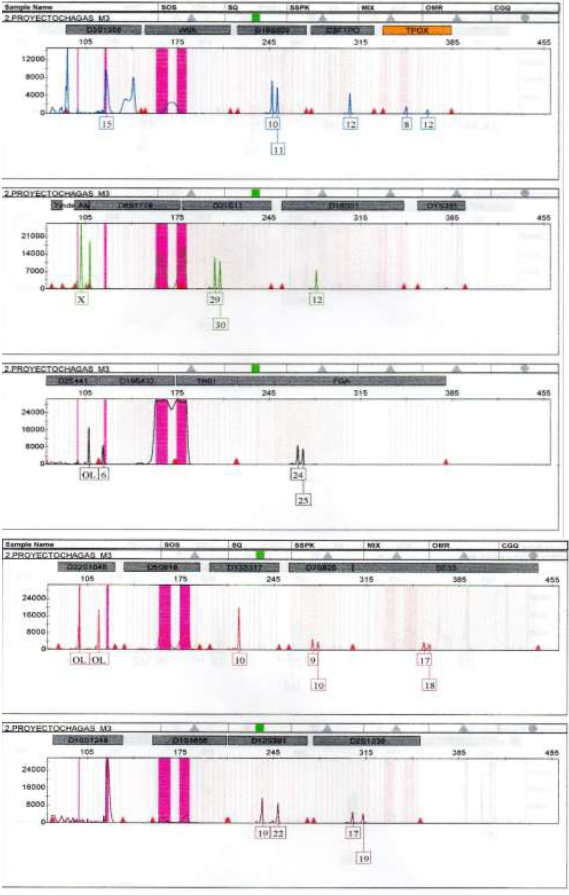
Figura 1 Electroferograma del análisis de STRs y electroforesis capilar de un perfil genético parcial correspondiente a un individuo de sexo femenino
El electroferograma de la figura 1 muestra los resultados del análisis de STRs realizado mediante electroforesis capilar, lo cual, permitió la separación y visualización de los fragmentos de ADN amplificados correspondientes a los diferentes loci STR. Esta técnica fue seleccionada por su alta especificidad en la identificación de perfiles genéticos humanos. Si bien existen otros métodos con alta sensibilidad para la detección general de ADN humano, como la amplificación de regiones conservadas del ADN mitocondrial, PCR convencional, qPCR con sondas específicas o análisis por heteroduplex, el presente estudio no tuvo como objetivo comparar dichas metodologías, sino aplicar un enfoque exploratorio centrado en la identificación puntual de origen humano en muestras de contenido gástrico de triatominos adultos; sin embargo, se reconoce que futuros estudios comparativos podrían contribuir a optimizar las estrategias de detección en contextos similares. En esta figura, se observa un perfil genético parcial obtenido de la muestra analizada (M2). Cada pico del electroferograma representa un alelo en un locus STR específico. La altura e intensidad de los picos reflejan la cantidad de ADN presente en la muestra. El perfil parcial indica que algunos loci no se han detectado o presentan señales de baja calidad, posiblemente debido a problemas con la integridad del ADN. El marcador de sexo, Amelogenina, confirma que el ADN pertenece a un individuo de sexo femenino.
La escasa información bibliográfica sobre la identificación de sangre humana en el contenido gástrico de T. infestans mediante análisis de STRs resalta la relevancia de los resultados obtenidos en este estudio para la comprensión epidemiológica de la enfermedad de Chagas. De las seis muestras analizadas, solo una proporcionó un perfil genético parcial, mientras que las demás no presentaron material genético humano. Esto podría deberse a la falta de alimentación de los insectos con sangre humana o a la baja cantidad de ADN humano, incluso utilizando la técnica robusta de PCR Multiplex con el kit GlobalFiler™. La muestra que sí generó un perfil genético confirma que al menos uno de los insectos se alimentó de sangre humana, lo que tiene importantes implicaciones epidemiológicas en la zona estudiada.
La baja tasa de éxito en la obtención de un perfil genético completo podría explicarse por varias razones, como la degradación del ADN (Solano-Florez, 2009) o la presencia de inhibidores en el contenido gástrico de los insectos que interfieren con la amplificación del ADN durante la PCR (Sandoval, 2014). Otros factores, como el tiempo transcurrido desde la ingesta de sangre o la cantidad limitada de ADN humano, también podrían haber influido.
La detección de un perfil genético humano, aunque parcial, destaca la interacción entre T. infestans y los humanos en entornos periurbanos, lo que es particularmente relevante en la comunidad de Huajchilla, del Municipio de Mecapaca, situada a más de 3000 metros sobre el nivel del mar, una altitud poco común para el habitat de este vector. Este hallazgo es crucial para comprender los patrones de alimentación de T. infestans y su posible papel en la transmisión de T. cruzi en zonas donde antes no se había identificado su presencia.
En este contexto, resulta importante considerar los estudios realizados por Breniere y colaboradores (2012, 2016), quienes investigaron la circulación de T. cruzi en vectores silvestres y domiciliarios en los valles interandinos del departamento de La Paz, incluyendo el municipio de Mecapaca. Estos trabajos identificaron distintos Discrete Typing Units (DTUs) del parásito, principalmente Tcl y TcV, tanto en vinchucas como en mamíferos reservónos, lo que evidencia la coexistencia de ciclos silvestres y domésticos de transmisión en esta región. La detección simultánea de distintos DTUs en vectores procedentes de entornos diversos respalda la hipótesis de una dinámica epidemiológica compleja, en la que T. infestans actúa como puente entre ambientes silvestres y humanos. En este marco, se resalta la relevancia del hallazgo de sangre humana en un vector capturado en un entorno semi-silvestre, como se reporta en el presente estudio.
Aunque los factores de riesgo asociados a la enfermedad de Chagas son variados y no siempre incluyen la ocupación de las personas (Chocho, 2023), la exposición de mujeres que realizan actividades agrícolas en áreas semi-silvestres, como la recolección de plantas medicinales, subraya la necesidad de intervenciones educativas y preventivas. La confirmación de que T. infestans se alimenta de humanos en áreas periurbanas tiene importantes implicaciones para la salud pública, ya que el riesgo de transmisión del parásito en estas zonas puede estar subestimado debido a sus características geográficas y sociodemográficas. Esto sugiere la necesidad de estrategias de control de vectores que aborden tanto entornos domésticos como silvestres.
Estos resultados son coherentes con estudios anteriores que subrayan la importancia de identificar la fuente de sangre en triatominos para comprender su papel en la transmisión de T. cruzi (Briceño y col., 2014; Peña-Callejas y col., 2023). La presencia de ADN humano en el contenido gástrico de T. infestans sugiere un contacto directo con humanos en áreas periurbanas, lo que aumenta el riesgo de transmisión de la enfermedad.
Si bien el proyecto IDH 3031 identificó la presencia de T. cruzi en algunos triatominos, este estudio detectó sangre humana en solo una muestra, lo que limita la generalización de los resultados. Se recomienda realizar estudios adicionales con un mayor número de muestras y en otras áreas periurbanas cercanas a la ciudad de La Paz para validar y expandir estos hallazgos, especialmente en relación con la adaptación de T. infestans a la altitud.
CONCLUSIONES
El análisis molecular del contenido gástrico de T. infestans mediante STRs detectó ADN humano en una de las seis muestras, identificando a una persona de sexo femenino como la fuente de alimentación. Este hallazgo subraya la interacción directa entre T. infestans y humanos en áreas periurbanas, ampliando el riesgo de transmisión de la enfermedad de Chagas más allá de los entornos domésticos tradicionales.
La detección de un perfil genético incompleto en la muestra positiva podría deberse a la presencia de inhibidores en el contenido gástrico, la degradación del ADN, o la limitada cantidad de material genético, lo que resalta la necesidad de optimizar las técnicas de extracción y amplificación.
El hecho de que T. infestans se alimente de sangre humana en entornos periurbanos es particularmente significativo en la comunidad de Huajchilla, ubicada a más de 3000 metros sobre el nivel del mar, donde las condiciones ambientales son distintas a las de su habitat típico. Además, la exposición de mujeres en actividades agrícolas semi-silvestres refuerza la necesidad de intervenciones preventivas específicas, ya que la presencia del vector en estas áreas podría implicar un riesgo de transmisión de T. cruzi más amplio de lo esperado.
Para mitigar estos riesgos, se recomienda ampliar las investigaciones a otras áreas periurbanas y considerar la variabilidad estacional y climática en la presencia de sangre humana. También es crucial implementar intervenciones educativas y preventivas dirigidas a comunidades expuestas, especialmente a aquellas involucradas en actividades agrícolas, para reducir el riesgo de transmisión de la enfermedad de Chagas y mejorar la salud pública en estas regiones.
Finalmente, si bien los hallazgos aportan información relevante sobre la interacción vector-humano en áreas periurbanas, el reducido tamaño muestral (6 muestras) limita la robustez estadística del estudio, por lo que los resultados deben interpretarse como indicativos y no concluyentes, requiriendo su confirmación con investigaciones que incluyan un mayor número de muestras.











 uBio
uBio